近日,我所董西洋研究员课题组与深海所合作在国际期刊《Scientific Data》在线发表了题为“Haplotype-resolved chromosome-level genome assemblies of the deep-sea annelid Lindaspio polybranchiata”的数据论文。该研究构建并公开了深海冷泉海稚虫科物种Lindaspio polybranchiata的单倍型分辨率染色体级基因组资源,相关基因组已被美国国家生物技术信息中心(NCBI)收录为该物种参考基因组,为深海冷泉生物比较基因组学、群体遗传学和环境适应研究提供了重要基础数据。
深海冷泉是海洋中重要的极端生态系统,具有高压、低温以及富含甲烷、硫化物等还原性物质的环境特征,孕育了特化的生物群落和复杂的生态过程。Lindaspio polybranchiata隶属于环节动物门海稚虫科(Spionidae),是南海冷泉生态系统早期演替阶段的典型先锋物种,能够快速定殖并形成高密度种群。该物种与冷泉环境关系密切,是研究深海化能合成生态系统演替和底栖动物环境适应的重要对象。
此前,该物种已有形态学、线粒体基因组和核基因组研究基础,但染色体级、单倍型分辨率的高质量基因组资源仍然缺乏,限制了其基因组结构、单倍型差异及适应性演化等研究的深入开展。基因组调查结果显示,该物种为二倍体,基因组杂合度达2.23%,重复序列比例约为52.39%。较高的杂合度和重复序列比例增加了基因组组装难度,也凸显了开展单倍型分辨率组装的必要性。
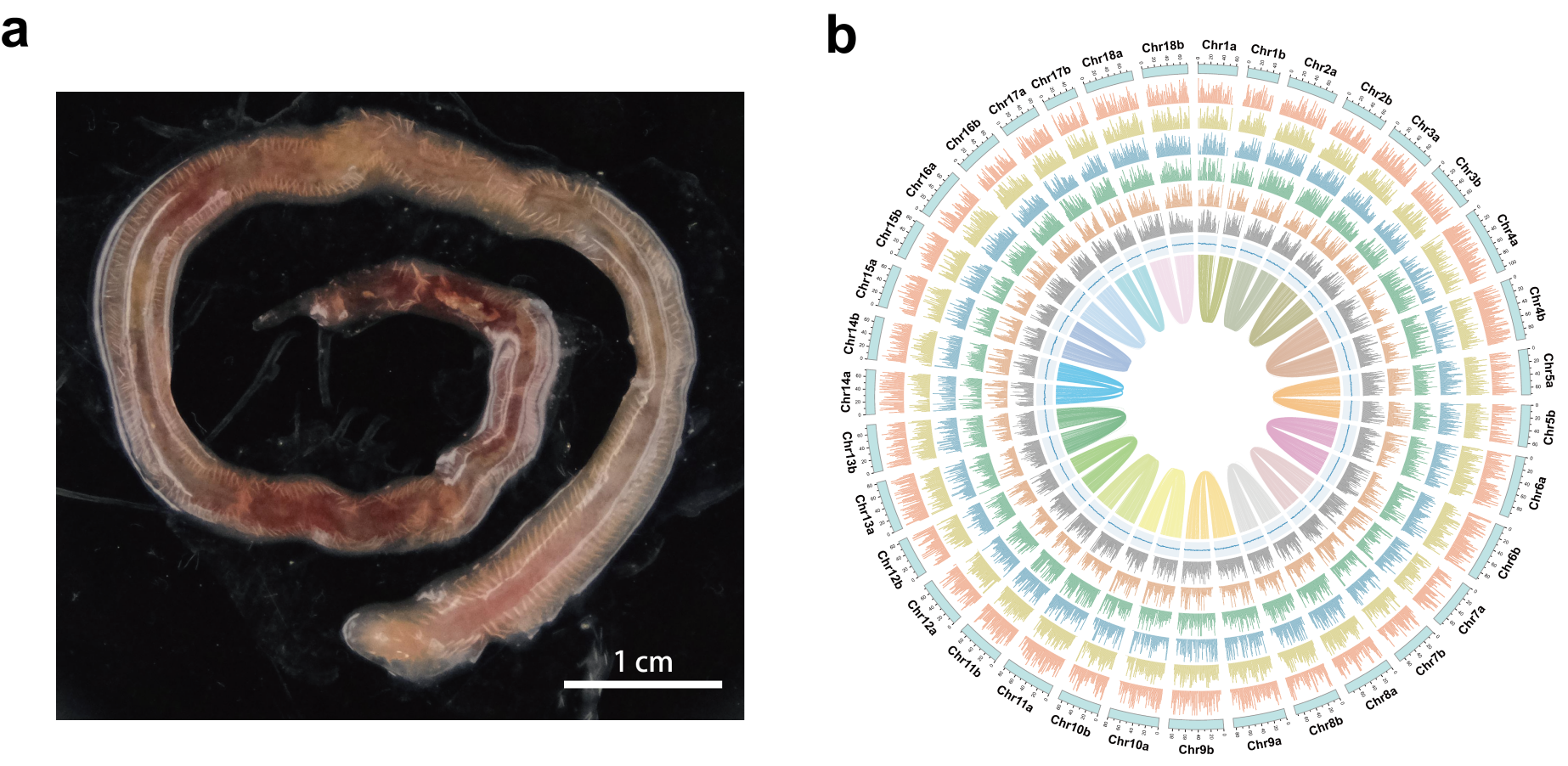
图1 Lindaspio polybranchiata个体及染色体级基因组特征
本研究样品采自南海北部陆坡海马冷泉。研究团队综合利用PacBio HiFi长读长测序、Illumina短读长测序、Hi-C染色质构象捕获技术和RNA-seq转录组测序数据,共获得290.20 Gb高质量测序数据。针对该物种二倍体、高杂合度和高重复序列比例等基因组特征,研究团队整合长读长测序数据和Hi-C数据,分别解析并组装出两个单倍型基因组,构建了单倍型分辨率的染色体级基因组资源。组装结果显示,两个单倍型基因组大小分别为1.72 Gb和1.38 Gb,均构建为包含18条伪染色体的染色体级基因组,scaffold N50分别达到76.1 Mb和71.0 Mb;BUSCO完整性分别达到91.2%和91.7%,表明组装结果具有较高完整性和可靠性。
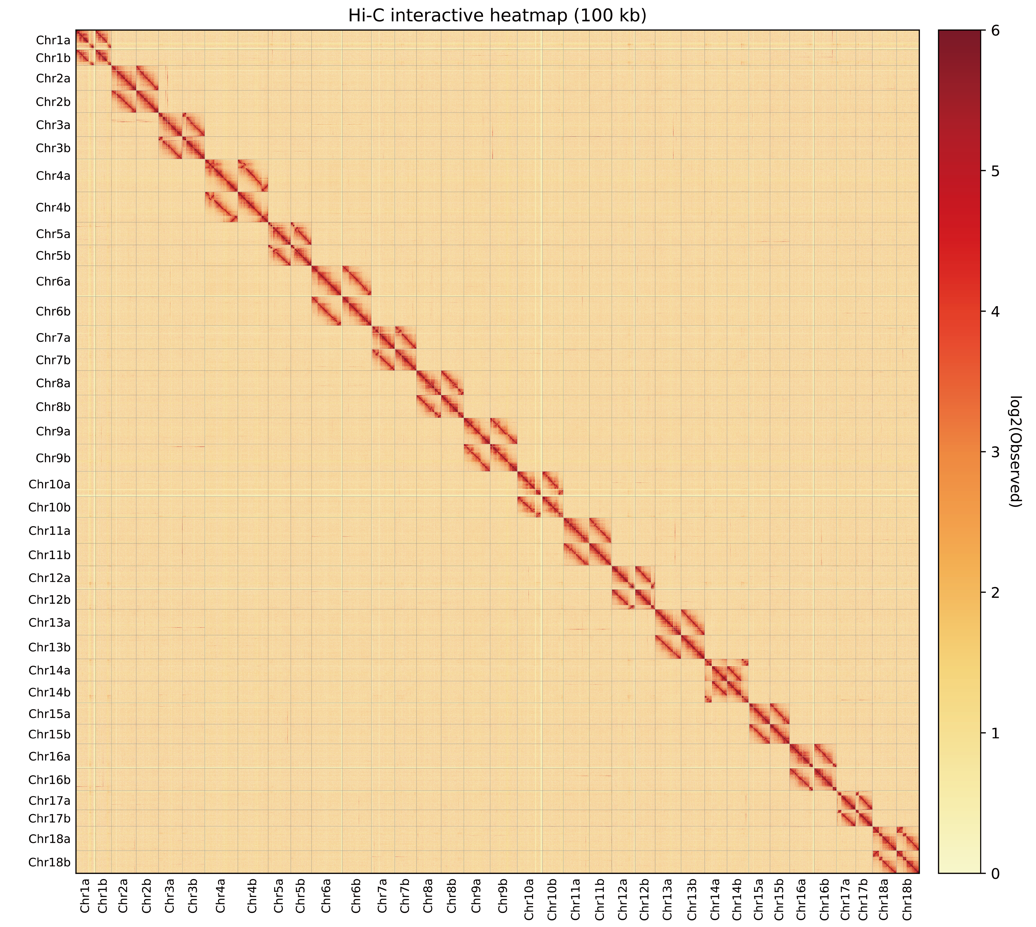
图2 Hi-C互作热图支持Lindaspio polybranchiata染色体级基因组组装
进一步的染色体共线性分析显示,两个单倍型在染色体尺度上整体保持较强共线性,共识别到9,173个共线性区域,总长度约469 Mb;同时也检测到丰富的局部结构差异,包括倒位、易位和重复区域等。这些结果为解析该物种单倍型间遗传差异、染色体结构演化以及深海环境适应相关基因组特征提供了重要数据基础。
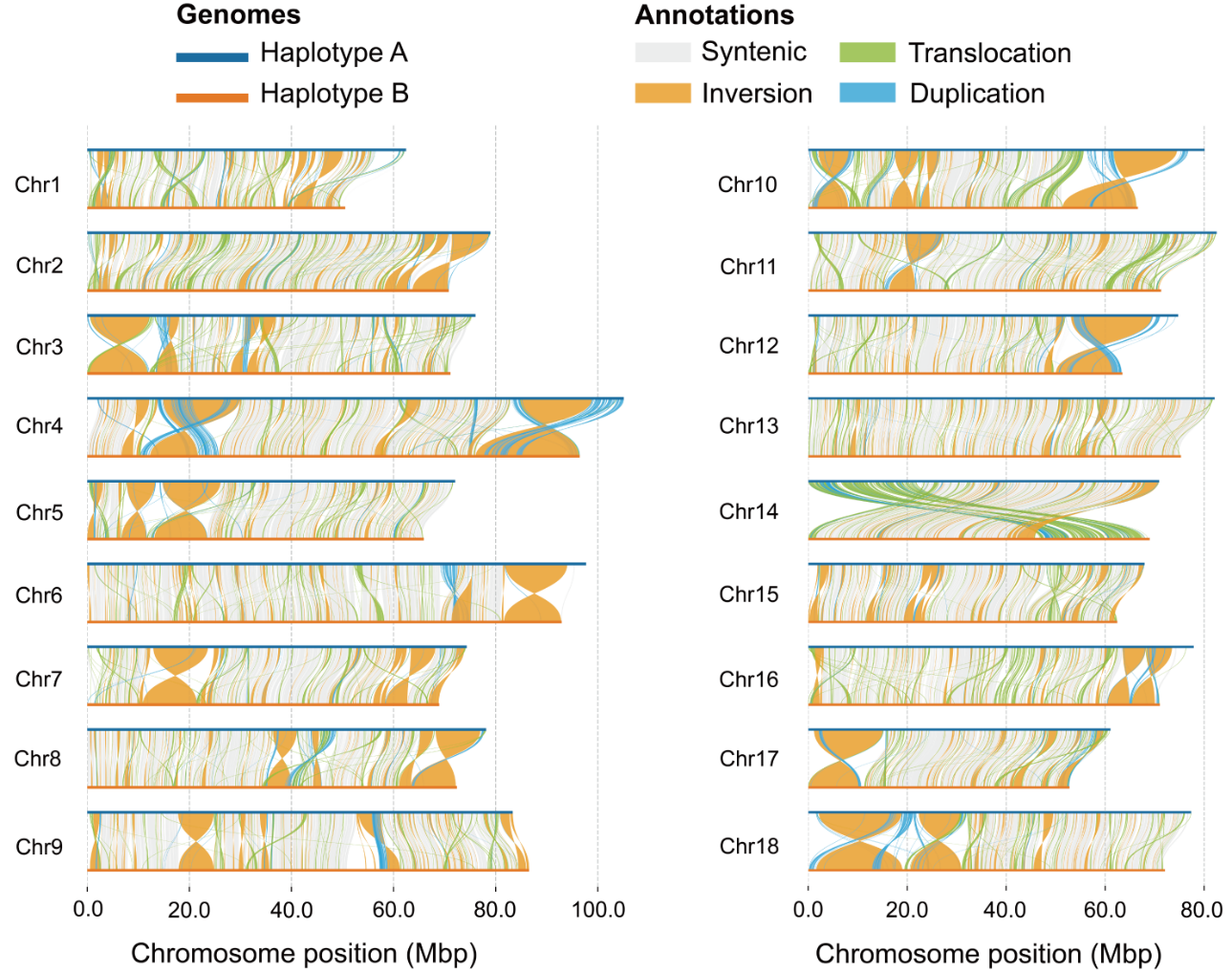
图3 两个单倍型基因组间的染色体共线性与结构变异
相关数据已开放共享至国家基因组科学数据中心(NGDC)、欧洲核苷酸档案库(ENA)、NCBI GenBank和figshare等公共平台,涵盖原始测序数据、基因组组装序列、注释文件和蛋白序列等资源,便于国内外科研人员开展后续分析和资源利用。
论文第一作者为海洋三所卢梓健博士研究生与深海所冉海力博士研究生,通讯作者为深海所高兆明研究员和海洋三所董西洋研究员。该研究得到福建省自然科学基金、厦门市自然科学基金项目、国家自然科学基金和海洋三所科研基本业务费等资助支持。
论文链接:https://doi.org/10.1038/s41597-026-07373-2